IF 11.2!恭喜南京医科大学联合“国自然”用GWAS+孟德尔随机化拿下双一区TOP!
- 2026-04-29 19:18:28


🔔全球超 16.9 亿人受慢性肝病困扰,南京医科大学团队在《Genome Medicine》发布跨祖先研究成果!
💡研究涵盖四大族群超 45.6 万人,聚焦 7 类肝功能生物标志物,挖掘出 5507 个遗传信号(含 210 个新信号),定位 2012 个潜在致病变异。团队独创 mdS2G 基因关联框架,锁定 1166 个关键基因,发现 PEPD 蛋白可降低代谢相关脂肪肝、肝硬化风险,为肝病靶向治疗提供新靶点与研究思路。
覆盖东亚、欧洲、南亚、非洲四大族群超 45.6 万人,突破单一族群研究局限。
开发 mdS2G 多维框架,整合三类证据锁定 1166 个可信基因,肝细胞富集效果更优,开源供学界使用。
证实肝 - 肠轴作用,发现 12 种肠道微生物对肝功能有因果效应;多效性变异与代谢、肿瘤等多系统表型相关。
发现 PEPD 蛋白可降低代谢相关脂肪肝、肝硬化风险,为肝病靶向治疗提供新候选分子。
想要GWAS+孟德尔随机化,关注精品生信,顶刊论文就在前方等你!

慢性肝病全球影响超 16.9 亿人,年死亡约 200 万,但其遗传机制仍未完全明确,且普遍存在诊断不足问题,制约了相关遗传研究。
以往肝功能相关全基因组关联研究(GWAS)多孤立分析生物标志物,且过度聚焦欧洲人群,缺乏跨祖先多样性,导致结果普适性受限。
同时,不同人群连锁不平衡差异等因素易引发异质性偏差,而整合多生物标志物挖掘多效性变异的研究较少,亟需通过跨祖先、多维度分析填补上述研究空白。
数据来源:
整合中国 HOPE 队列与英国生物银行数据,覆盖东亚、欧洲等四大族群超 45.6 万人,纳入 7 类肝功能生物标志物检测数据。
技术平台:
采用 Illumina 芯片测序,结合 SHAPEIT4、MINIMAC4 等工具进行基因分型与填充,依托 Tabula Sapiens 等数据库获取单细胞测序数据。
分析方法:
以跨祖先 GWAS 荟萃分析为核心,辅以精细定位、PheWAS、孟德尔随机化等技术,创新 mdS2G 基因关联框架,整合多维度证据实现遗传信号与基因的精准链接。


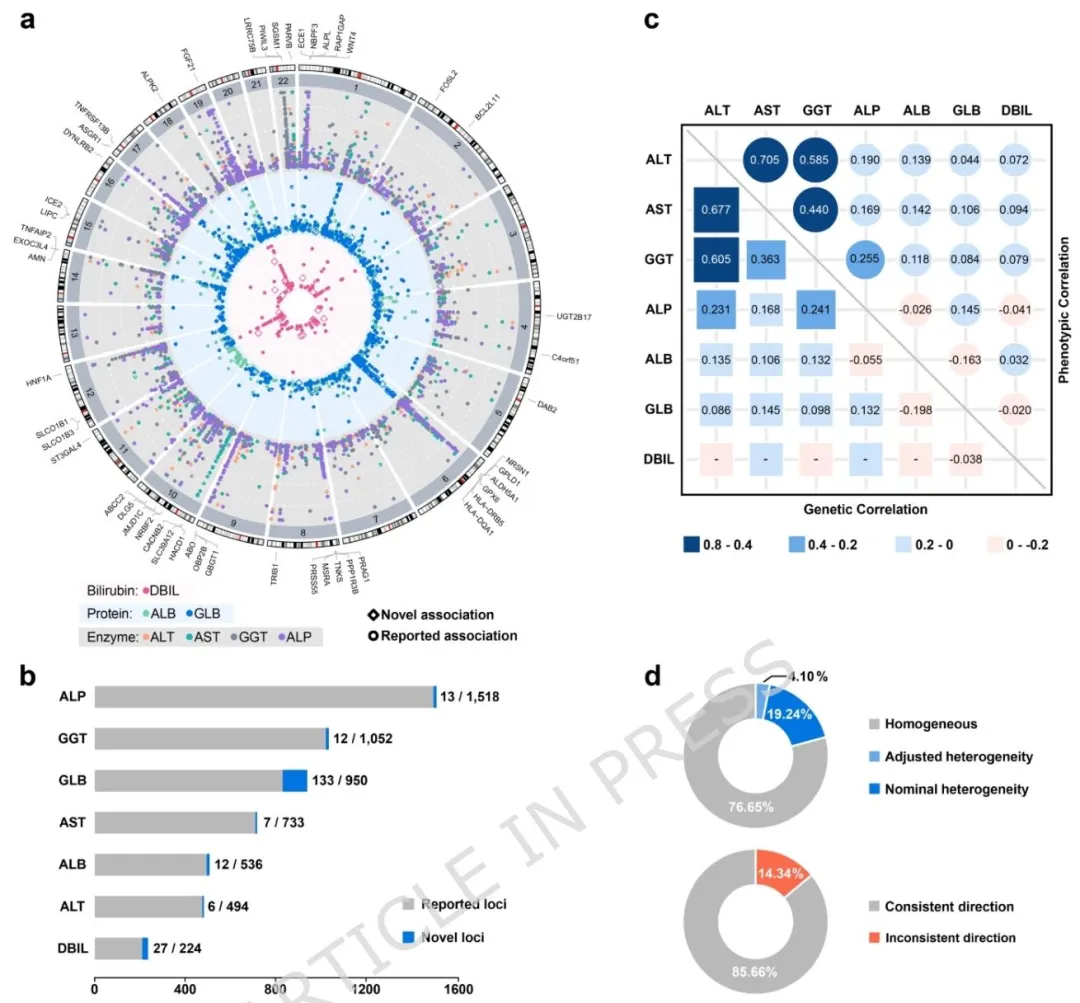
图一 七种肝功能相关定量生物标志物的跨祖先全基因组关联荟萃分析

图二 跨祖先连锁不平衡参考面板提升精细定位分辨率及跨祖先一致性
多系统关联解析
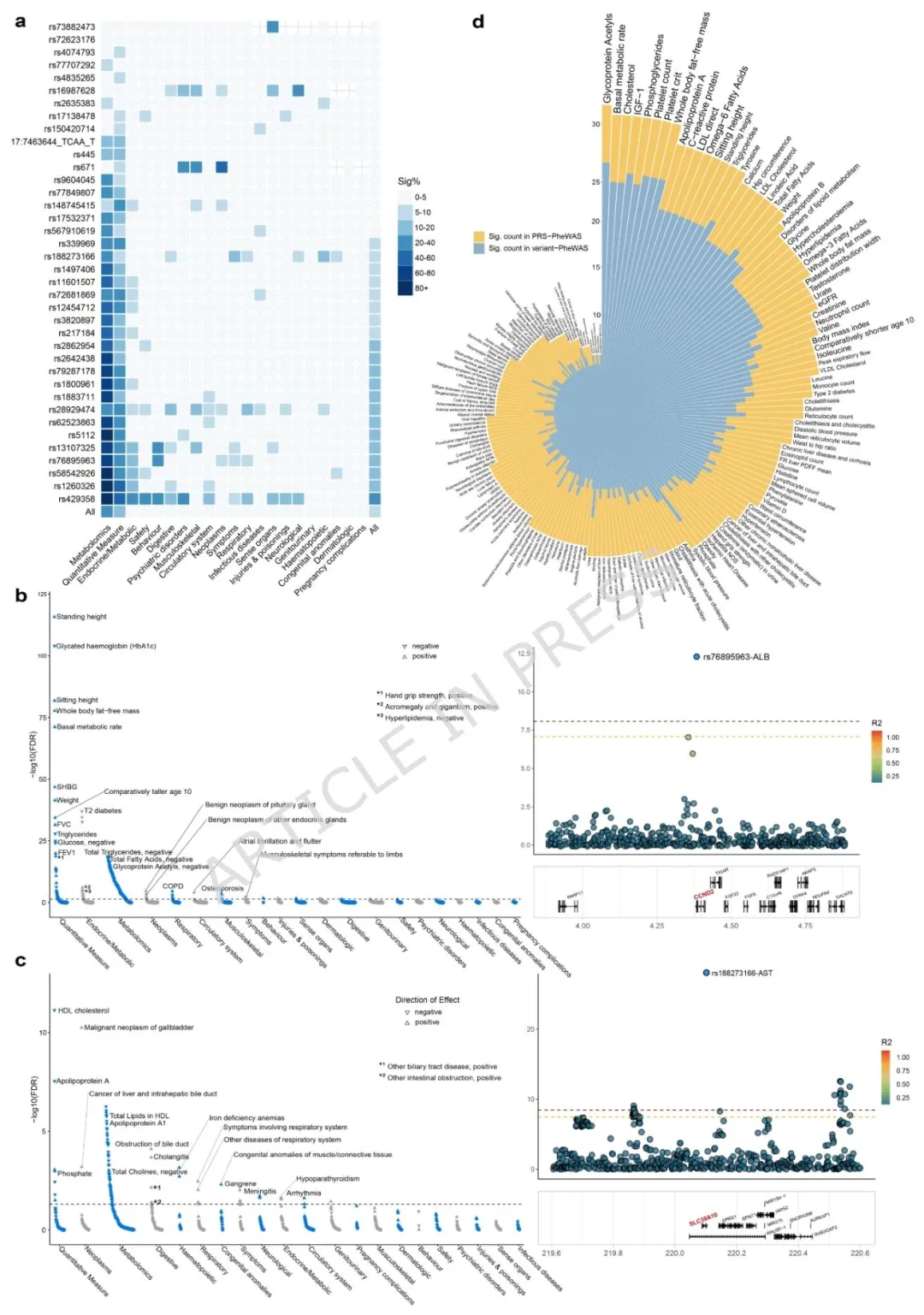
图三 38 个多效性变异的表型全关联分析
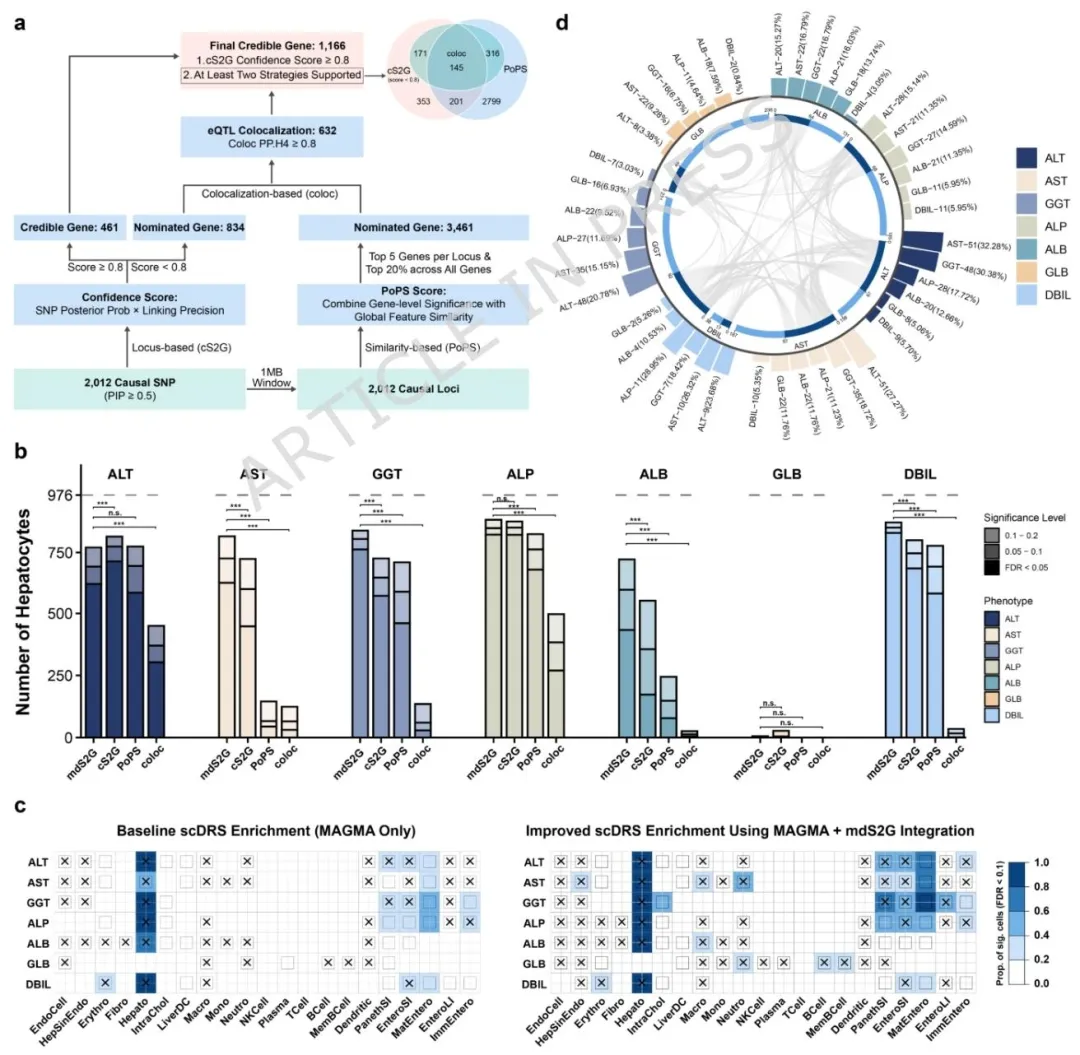
图四 利用 mdS2G 框架筛选出七种肝功能相关定量生物标志物的 1147 个可信基因
这项跨四大族群的肝功能遗传研究成果丰硕!通过超 45.6 万人的 GWAS 荟萃分析,挖掘出 5507 个遗传信号(含 210 个新信号),精准定位 2012 个致病变异。
创新 mdS2G 框架锁定 1166 个关键基因,证实肝 - 肠轴重要作用,更发现 PEPD 蛋白可降低代谢相关脂肪肝、肝硬化风险。
研究打破单一族群局限,为肝病精准防治提供全新遗传靶点,开源工具也为后续研究奠定基础,助力肝脏健康进入精准医疗时代。
想用GWAS+孟德尔随机化进行生信分析get同款思路?欢迎联系精品生信,定制专属你的高分论文!


公共数据库 机器学习
孟德尔随机化 多组学
专业数据分析




