南京大学等EST:机器学习赋能拉曼传感阵列:30 分钟快速精准检测水中磺胺类抗生素
- 2026-04-10 05:03:36
机器学习赋能拉曼传感阵列:30 分钟快速精准检测水中磺胺类抗生素

近日,南京大学研究团队在Environmental Science & Technology发表突破性研究成果,提出多底物表面增强拉曼光谱(SERS)融合策略,结合机器学习实现水环境中磺胺类抗生素的快速识别与精准定量,为现场环境监测提供全新技术范式。
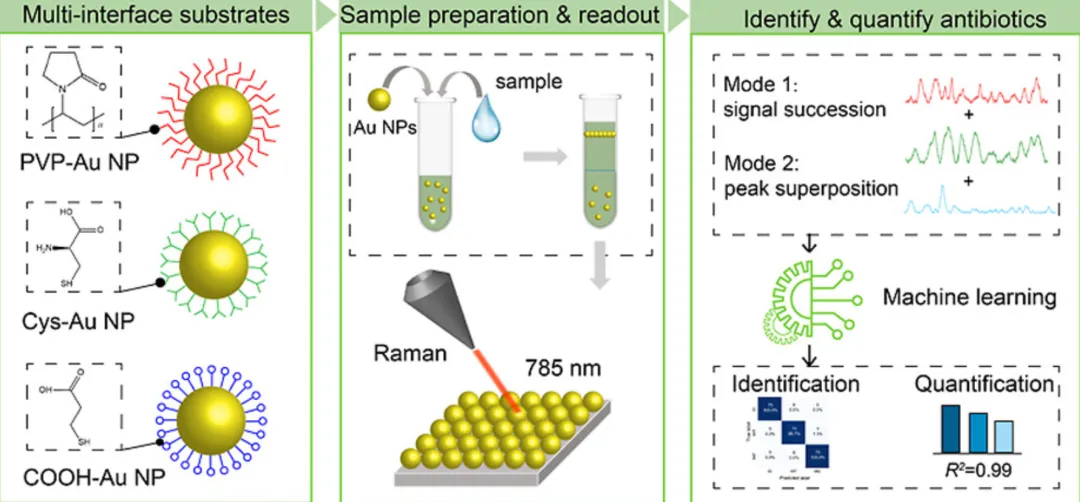
抗生素作为典型新型污染物,广泛存在于河流、湖泊与市政污水中,长期低浓度暴露会诱导微生物耐药性,威胁生态安全与公众健康。传统液相色谱‑质谱(LC‑MS)虽精准,但前处理繁琐、仪器昂贵,难以满足现场快速检测需求;单一底物 SERS 则面临结构相似物区分度低、复杂基质干扰强等瓶颈。
针对上述痛点,团队构建双模式响应 SERS 传感阵列:采用聚乙烯吡咯烷酮(PVP)、L‑半胱氨酸(Cys)、3‑巯基丙酸(MPA)分别功能化金纳米颗粒,制备三种互补响应底物,形成信号接替与峰叠加两种拉曼响应模式。其中,PVP‑Au 体系随抗生素浓度升高发生配体交换,基底信号减弱、待测物信号增强;Cys‑Au 与 COOH‑Au 体系因强 Au‑S 键保持基底信号,与抗生素特征峰叠加,大幅提升光谱信息维度。
研究将三种底物光谱级联构建多界面融合光谱(MICS),结合支持向量机(SVM)、多层感知机(MLP)等机器学习模型,同步实现磺胺嘧啶(SD)、磺胺二甲嘧啶(SMT)、磺胺甲恶唑(SMZ)的定性识别与定量分析。数据显示,该方法对单一污染物识别准确率从 95%–96% 提升至99.6%,混合污染物准确率从 82.2%–92.2% 提升至96.7%;定量预测决定系数 R² 最高达0.99,预测误差显著降低。
在河水、湖水、市政污水二级出水等实际水体中,方法加标回收率为75.5%–116%,中位数达 97.5%,27 组测量中 23 组落在 80%–110% 区间,从样品前处理到结果输出仅需约 30 分钟,适配现场快速检测场景。
该研究突破单一 SERS 底物信息维度限制,通过多底物阵列 + 机器学习协同,解决结构相似污染物难区分、复杂基质定量不准的行业难题,为水中抗生素等新型污染物现场监测提供高效、低成本解决方案,有望推广至更多环境污染物快速检测领域,支撑水环境安全预警与源头管控。
APA 引用
Yang, Y., Shan, C., & Pan, B. (2026). Rapid identification and quantification of aqueous antibiotics over a machine learning‑integrated Raman sensor array. Environmental Science & Technology. https://doi.org/10.1021/acs.est.6c00577

| #抗生素 | #微塑料 | #全氟化合物 |
| #有机磷酸酯 | #新污染物分析技术 | |
| #内分泌干扰物 | #新污染物处理技术 | #科研动态 |
