通过MISTy框架分析细胞空间共定位,发现KRAS突变肿瘤中Epi_01与Mono_S100A8呈强烈共定位,而野生型中该关系较弱(图4A)。进一步构建同型细胞网络显示,突变组中Epi_01与Mono_S100A8的网络在空间上紧密交织,而Fib_CTHRC1的网络部分重叠于二者周围,提示其可能形成物理屏障(图4B)。野生型肿瘤缺乏Mono_S100A8和Fib_CTHRC1的网络,说明该空间结构为KRAS突变所特有。
图4. KRAS突变型与野生型结直肠癌组织中的细胞类型共定位及同型细胞相互作用程度
基于细胞组成聚类识别出6个空间生态位,其中CC5高度富集Epi_01与Mono_S100A8,集中分布于KRAS突变肿瘤的核心区,定义为KRAS突变特异性生态位(图5A)。CC6则以Fib_CTHRC1及大量CD4+/CD8+淋巴细胞为主要成分,呈周边环绕分布,可能作为纤维屏障排除淋巴细胞浸润(图5B-C)。野生型肿瘤中未见CC5和CC6结构,进一步证实该空间组织模式为KRAS突变所特有。
图5. KRAS突变型与野生型结直肠癌组织中的组成簇及其细胞组成
KRAS突变组中Epi_01、Fib_CTHRC1、Mono_S100A8呈高频空间邻接并形成紧密网络,野生型组中该网络完全缺失。证实Fib_CTHRC1在外周形成物理屏障,三者共同构建KRAS突变特异的免疫抑制生态位【图6】。
图6 KRAS突变型与野生型结直肠癌组织中的异型细胞相互作用及空间分布
构建KRASG12D/+;Villin-Cre小鼠,证实突变组中Fib_CTHRC1和Mono_S100A8比例显著升高,与突变上皮细胞通过MDK-SDC4和胶原-整合素信号轴互作(图7)。
mIHC进一步验证CEACAM1、CTHRC1、S100A8在KRAS突变组织中空间共定位,且CTHRC1呈环绕分布,形成免疫抑制屏障(图8)。
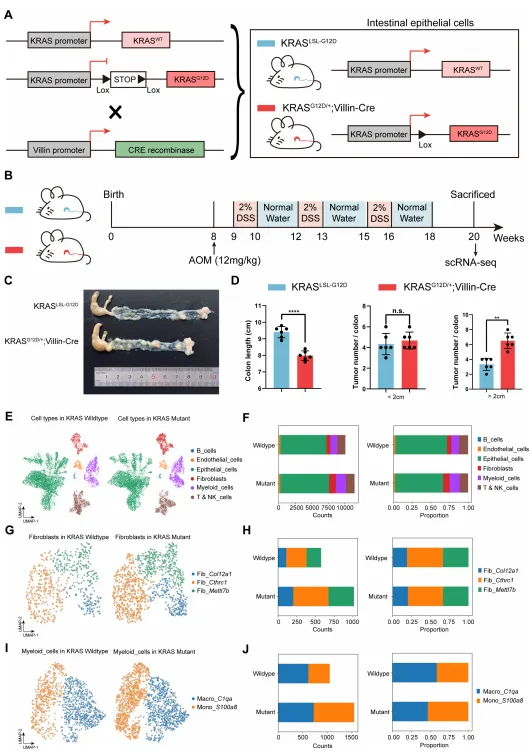 图7. Fib_CTHRC1和Mono_S100A8在KRASG12D/+ Villin-Cre小鼠中发挥关键作用
图7. Fib_CTHRC1和Mono_S100A8在KRASG12D/+ Villin-Cre小鼠中发挥关键作用
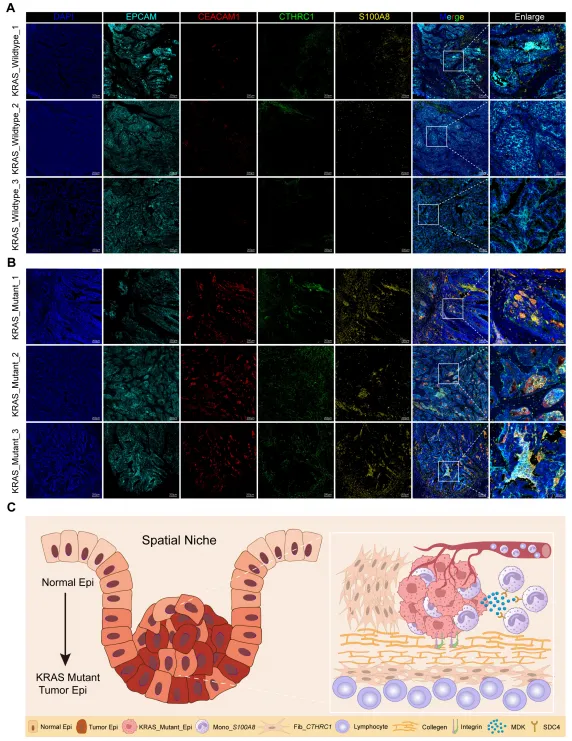 图8. 细胞标志物的空间分布及KRAS突变TME的拟议模型
图8. 细胞标志物的空间分布及KRAS突变TME的拟议模型